基于 NMR的代谢组学研究
- 2012-12-07
- 专题
代谢物是生命过程中发生的生物化学反应的产物,能够从某种程度上反映生命过程的本质。虽然人们对代谢物和代谢水平的认识和研究已经有上百年的历史,但是,将生物体作为一个整体进行研究的代谢组学(metabonomics/metabolomics),成为分子病理、基因功能分析和系统生物学研究的强有力的技术平台只有7年的历史。1998年Tweeddale等[1]在研究大肠杆菌的代谢时提出了代谢组(Metabolome)这个概念用来表示代谢物整体(total metabolite pool),并且指出,代谢组分析能够提供有关细胞代谢和调控的信息。Nicholson等[2]在1999 年提出代谢组学的概念(metabonomics)时将其定义为:对病理/生理刺激或基因改变时生物体系的动态代谢响应的多参数定量分析(the quantitative measurement of the dynamic multiparametric metabolic responses of living systems to pathophysiological stimuli or genetic modification)。Metabonomics一词来自希腊文的词根“meta”和“nomos”。“meta”意思是“变化(change)”,“nomos”意思是“规律”或“原则”(就象 economics)。从这个定义本身不难看出,代谢组学分析的对象是生物体本身,而且是一个动态的整体。Nicholson研究组的工作包括动物体生理[3~5]、药物毒理[6~9]、分子表型学[10,11]、疾病诊断[12~14]和以系统生物学为基础的功能基因组学[15~17]。Fiehn等[18]在2000年,Raamsdonk 等[19]在2001 年又提出了metabolomics这个单词,用以强调把代谢组学这个技术平台用于研究细胞系统基因的功能。目前,metabolomics有多个定义,但其本质是:给定细胞在给定时间和环境下的所有小分子代谢物的定量分析(the quantitative measurement of all low molecular weight metabolites in an organism's cells at a specified time under specific environmental conditions)。所以从定义来看,metabolomics指的是静态生物体系代谢组分析,因此可以认为是 metabonomics 的一部分。事实上,近年来也有动态代谢组学(dynamic metabolomics)[20]提法出现,说明metabolomics的含义正在朝着metabonomics靠近。在中文的表述中,没有必要将两个名词分开,一律用“代谢组学”以避免不必要的名词混淆。2002年以来,Nicholson等[21]和Fiehn等[22]分别撰写综述文章从不同的角度阐明代谢组学是研究药物毒性和基因功能的平台技术,以及联结基因型和性状表型的有力工具。这一系列论述奠定了代谢组学的基础。代谢组学的出现,主要得益于分析技术的发展使得对大量样品和大量代谢物的快速定量测定成为可能,而最为常用的方法是核磁共振(NMR) 和质谱(MS)(图1) 。
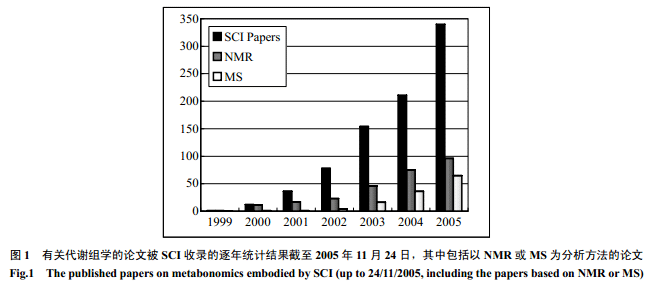
1 代谢组学的发展趋势
代谢组学是一个全新的研究热点。这主要表现在:第一、代谢组学的研究论文数正在以指数方式增长(图1);第二、高影响因子(>8.0) 学术刊物上发表的论文数量较多(>60 篇)[17~19,21,23~81];第三、核心论文引用率高,其中引用100 次以上的有6篇,单篇最高引用接近240 次;第四、研究范围广泛并不断增加,涉及到功能基因组学、营养学、病理学、药理学、毒理学、植物学、微生物学以及系统生物学等众多领域;第五、仪器和分析技术的快速发展为代谢组学的进步提供了更加广阔的空间,也就带来了更多的挑战和机会。不断提高的磁场强度使得核磁共振谱仪的分辨率有了更进一步的提升,超低温探头的出现也让 NMR的检测灵敏度有了一定程度的提高。自动进样技术极大的缩短了大批量样品的检测时间。而计算机技术的飞速发展为数据分析的速度和可靠性提供了更有力的支撑。
2 代谢组学与基因组学、蛋白质组学的关系
代谢组学研究的是在病理生理刺激或基因改变条件下生物体系代谢水平的应答,此前提出的基因组学和蛋白质组学则分别从基因水平和细胞蛋白表达水平研究生物体系对药物刺激的响应。每个物种的基因组所含的基因序列与基因数目相对固定,但这些基因的表达水平会随着发育阶段不同或外部条件的变化而变化。从药物研究和毒理学的角度来看,基因组学研究的是生物体受外源性药物刺激后基因表达的改变,然而基因表达的改变或者调节与细胞系统整体功能之间的关系尚不清楚。因此蛋白质组学方法主要针对给药或其它病理生理过程引起的细胞蛋白质组成的变化进行半定量测量[82~84]。尽管与基因组学相比,蛋白质组学研究不那么昂贵,但是由于蛋白质数量众多,现有蛋白组学手段通量有限,因此劳动强度较大,进展缓慢。同时必须指出,基因组、转录组和蛋白质组研究更强调生命过程的调控机制和物质基础,而代谢组是以体内生物化学反应的产物的整体变化为出发点来研究生命过程的本质。事实上,多数哺乳动物(如人)是动物体本身(宿主)和消化系统微生物菌群共同进化、协同工作的“协同生物体”(symbiotic species)[85],对宿主本身的基因,蛋白质的认识只是该体系的一小部分[86]。因此,基因组、转录组、蛋白质组和代谢组是从不同层面和水平上研究生命过程的途径。
基因和蛋白质数量众多,它们的功能除了与一级和二级结构有关外,在更多情况下与它们的三级结构、动力学过程和相互作用有关。这也是功能基因组学和功能蛋白质组学研究的重点。与此形成对比的是,代谢物分型要少得多。目前已知的代谢物只有几千种。由于代谢物是生命过程的终端产物,不仅分子量小而且在所有的生物体中都是相同的,因此,一般不存在三维结构和动力学的问题,也不要求完整的基因序列或者庞大的 EST(Expression Sequence Tag)数据库。基因和蛋白表达具有重复性,由此导致的代谢物或代谢水平的变化则具有累加性。这种含量上的放大效应,使得代谢物的识别比基因或蛋白质的识别要容易得多。有限的代谢物分型必然导致一种代谢物同时涉及多个代谢过程或代谢循环。每个代谢循环会产生多个代谢物,不同代谢循环之间相互联系、互相影响。代谢组学正是从代谢物整体变化的角度来研究生物体对各种刺激的动态响应。
3 代谢组学研究方法
体液中的代谢物质与细胞以及组织中的代谢物质处在一个动态的平衡当中,所以当机体由于毒性或代谢障碍导致组织细胞出现异常的时候,生物体液的组成就会产生变化。代谢组学研究方法就是检测代谢物水平的整体和动态变化,提取潜在的有诊断或常规程序化价值的生化信息,以此来反映生物体在外源刺激作用下真实的体内的生物学过程,建立“组学”参数的输入与响应输出之间的联系。
代谢物整体水平的检测所依赖的方法是分析化学中的各种谱学技术,如核磁共振波谱、质谱、高效液相色谱、红外光谱、紫外可见光谱以及各种原子光谱等。对海量谱学数据进行统计和归类分析,从中提取代谢特征或代谢时空的整体变化规律,是分析化学中的化学计量学或化学信息学的研究范畴。值得指出的是,代谢组学所强调的代谢特征或代谢时空的整体变化,不是传统意义上的某种代谢物或少数几种代谢物含量和存在方式的变化。建立代谢特征或代谢时空的变化与生物体特性的变化之间的有机联系,是代谢组学研究的最终目标。因此,分析化学在代谢组学研究中发挥着非常重要的作用,甚至是不可取代的作用。
3.1 代谢组学的研究过程
代谢组学研究一般包括四个步骤:第一步,给予生物体一定的刺激。这种刺激可以是基因的变异、剔除或引入,体内生物过程的催化或抑制,致病或致病物质(无机、有机、病毒、细菌、寄生虫等等)的引入,以及各种环境因素的改变等等。除了刺激因素之外,引入刺激的时间和强度等也需要精心设计。适合于代谢组学研究的样品种类非常广泛,可以说是无所不包,例如尿液、血液、组织或组织提取物、器官甚至整个生物体等等。样品收集时间、部位、种类等应给予充分考虑。第二步,代谢组数据的采集。用核磁共振、质谱、色谱等分析手段测定其中代谢物的种类、含量和状态以及其变化。第三步,建立表征代谢特征的时空模型[87]。在代谢组学中最常用的建模方法是主成分分析(Principle Components Analysis, PCA)。PCA 是对多变量数据进行统计处理的一种数据线性投影方法,它在保留原有信息的基础上将高维空间中的样本投影到较低维的主成分空间中。其基本思路是以一种最优化方法浓缩数据,寻找几个由原始变量线性组合而成的主成分,以揭示原始数据的特征,提取基本信息,实现对数据的可视化和样本的分类聚集。用PCA 方法建立的以代谢物的种类、含量和状态随时间的变化为基础的代谢物时空模型应能够清楚地反映出外源性刺激的种类、程度和动态变化以及引起样本在时空模型中的不同分布的标志性代谢物。第四步,建立代谢物时空变化与生物体特性的关系,达到从不同层次和水平上阐述生物体对相应刺激的响应的目的。
3.2 基于 NMR的代谢组学的特点
作为众多化学分析方法中的一种,NMR在代谢物组学的研究中起着非常重要的作用。这主要取决于NMR所具有的优势:首先,用NMR分析生物体液等复杂混合物时样品的前处理简单,测试手段丰富,包括液体高分辨NMR、高分辨魔角旋转(HR-MAS)NMR 和活体核磁共振波谱(MRS),因此,能够在最接近生理状态的条件下对不同类型的样品进行检测。其中需要特别提到HR-MAS方法,该方法是将样品在与静磁场成魔角(54.7°) 的方向旋转,消除了磁场不均匀性、化学位移各向异性和偶极-偶极相互作用带来的谱线增宽影响,从而可以获得与液体高分辨 NMR相媲美的分辨率。更重要是,这种方法对代谢物在组织中的定位有独特的优点,目前已经有不少将此方法用于肝脏[88~90],脑组织[91~93],前列腺[94~96]等组织的研究报道。其次,NMR是一种无损的多参数和动态分析技术,NMR同时具有定性分析和定量分析功能,并且通过单次检测可以得到所有含量在NMR检测限以上的物质(含有 NMR可观测核的物质)的特征NMR谱,以及这些物质在整个刺激周期中的动态变化,而且NMR谱携带有丰富的分子结构和动力学信息;再次,NMR检测可以在很短的时间内完成(一般5~10 min),这对于实现高通量样品检测和保证样品在检测期内维持原有性质来说是至关重要的。此外,流动探头、自动进样技术和自动 NMR谱处理技术的出现和不断完善,也使得测定速度和准确性不断提高。而且,核磁共振手段灵活多变,通过操控脉冲序列我们可以获得多种多样的信息。例如代谢组学中常用到的谱编辑手段[88,97~99]:使用单脉冲、CPMG(Carr-Purcell-Meiboom-Gill)和扩散加权序列,可以分别获得样品中不同官能团、不同分子量或不同存在状态的分子的1H NMR谱。
当然NMR方法也有其局限性,例如它的检测灵敏度较低,而且检测动态范围有限,很难同时检测同一样品中含量相差很大的物质。色谱(LC)以其卓越的分离能力,质谱(MS)技术以其普适性、高灵敏度和专一性,也成为代谢组学中重要的分析手段,但是它们也存在各自的缺陷,如色谱和质谱的选择性检测能力较差、大量谱峰的识别以及方法的重现性问题、质谱中不同离子化程度对代谢物定量的影响等。
4 代谢组学研究的广泛应用
代谢组学经过几年的发展,方法正日趋成熟,其应用已经渗入生命科学研究的方方面面,并日益彰显出其强有力的科学潜能。
4.1 药物开发、安全性评价
快速发展的医药工业对分析手段的效率以及可靠性提出了更高的要求。药物直接或者通过某些代谢途径产生的代谢物使基因表达产生改变,基因表达的改变又会影响蛋白质的合成,基因与蛋白质的变化都可以造成毒理终点的产生;另外药物通过代谢进入血液,进而分布到一些组织器官产生作用,也能形成毒理终点。而毒理终点造成的生化改变是 NMR所能检测到的。对 NMR数据采用适当的化学计量学和多变量分析方法,就能提取出丰富的药物代谢信息。因此代谢组学在制药工业中发挥着巨大的作用:在药物开发阶段,代谢组学不仅可以进行早期活体毒理测试,而且能为药物分子的筛选提供依据;在药物临床应用前,它能帮助确定药物的安全性生物标记物和代谢表型,并能评价将动物模型实验应用于人类疾病的可行性。
Nicholson研究组多年的实验发现:基于NMR的代谢组学方法不仅能区分组织器官的正常与非正常的状态,而且能给出毒性作用的靶器官以及作用机制,识别出毒性的生物标记物。他们的工作主要集中在药物对肾脏、肝脏毒性的研究上,通过长期的实验经验积累,他们将体液的磁共振波谱分解成一系列的“生物标记物窗口”,这些“窗口”分别与特定的器官毒性相对应,从而可以从简单的1D1H NMR谱获取丰富的毒理信息[21]。在药物毒理代谢组学的研究领域,最为瞩目的工作是国际COMET(Consortium for Metabonomic Toxicology)计划[100,101],该计划由五家著名的制药公司与英国帝国理工学院联合完成,旨在用啮齿动物的尿液、血液的1H NMR谱建立代谢组数据库,并为目标器官及其位点的毒性建立预测性专家系统。在完成约147种毒性模型的实验研究后,他们已经建立起了第一个基于机器学习的实验室啮齿动物肝脏和肾脏毒性预测的专家系统。
4.2 病理学研究
由于病理状态造成的代谢紊乱同样也是核磁共振技术所能检测的,同时,机体任何部分出现异常状态,在体液的组成上都会有反映。
相对于传统的医疗诊断方法,代谢组学方法具有无创性及样品制备简单等优点,因此其应用范围涵盖了先天性代谢缺陷、肾脏和肝脏移植、Alzheimer疾病、癌症等广泛的领域[102~104]。其中典型的例子是冠心病的研究。冠心病以前主要通过血管造影术来诊断,该方法不仅昂贵,而且伴随有不良反应,甚至可能导致死亡。而 Brindle 等[25]用代谢组学方法用于冠心病诊断,结果显示经过正交信号校正(OSC) 的模式识别方法能很好的区分重症冠心病(三支血管疾病,TVD)和冠状动脉正常人的血清。另外,对于传统的测量血压、总胆固醇、总甘油三脂、纤维蛋白素原、白细胞数量等冠心病危险度因子(risk factor)无法区分的不同严重程度的冠心病,代谢组学方法也能很好的区分,并且通过回归分析,发现VLDL、LDL、HDL和胆碱等是导致两者区分的主要因素。他们也用代谢组学方法对不同程度的高血压病人作了研究[12],发现导致不同收缩压(Systolic Blood Pressure, SBP)的因素是血清中脂蛋白颗粒的组成,如脂肪酸侧链的不饱和度、脂蛋白分子之间相互作用的强度,而不是脂类的绝对含量。多种癌症[96,105](乳腺癌、卵巢癌、肝癌、前列腺癌、脑肿瘤)、先天性障碍[102~104]等疾病在代谢组学方法的指引下也有了许多新的发现。最近,wang等[44]用代谢组学方法研究了血吸虫病对啮齿动物尿液代谢的影响,发现血吸虫的侵染严重扰乱了体内三羧酸循环等代谢过程,并对肠道菌群的代谢产生了影响。可以预见,代谢组学在分子病理和疾病诊断等领域将有广阔的应用前景。
4.2 营养代谢组学
代谢组学的方法可以帮助识别和常量营养物的最终摄入效应密切相关的代谢物,并且有助于定义各种常量营养物的正常摄入范围。从长远来看,代谢组学的研究可以帮助理解当单一的养分(如氨基酸等)摄入过多或者过少时整个机体的新陈代谢会发生怎样的改变。除此之外,这也是一个在考虑到代谢的复杂性的基础上合乎科学地建立常量营养物的合理摄入范围的评估策略。
Solanky 等[106]对进食含有(结合态或非结合态)大豆异黄酮的食物的女性的尿液进行了检测。结果发现,由于大豆异黄酮的摄入,导致了尿液中的氧化三甲胺明显升高,对氧化三甲胺的升高有两种可能的解释:(1)动物实验表明大豆蛋白对损伤的肾脏有明显的保护作用,而氧化三甲胺含量的升高以及伴随发生的甜菜碱、胆碱、肌酸和肌酐含量的变化,标志着肾功能的增强;(2)氧化三甲胺、甜菜碱、胆碱等都是微生物代谢的中间产物,因此进食含有丰富大豆异黄酮的食物,可能扰动了肠道微生物菌群。谷氨酸和谷氨酰胺的上升表明三羧酸(TCA) 循环受到了影响,因为它们可以很容易转化成 TCA 循环的中间产物。另外柠檬酸的下降和糖含量的改变标志着糖酵解速率的下降,从而影响到糖类的代谢。而甲胺通路的中间产物以及胆碱、甜菜碱、甘氨酸和乙酸盐的含量变化表明脂类和胆固醇的代谢、转移发生了改变。以上结果显示出基于 NMR的代谢组学能够给出复杂生物体系对饮食改变的精细生化响应。
几个世纪以来,菊花茶作为一种功能性饮料一直为人类所饮用,起到抗炎、抗氧化和抗菌等保健作用。Wan g等[107]对持续饮用欧洲黄菊的志愿者的尿液进行了分析,通过正交信号校正的模式识别方法排除了性别、饮食的影响,提取出了仅仅和此花摄入有关的代谢信息。研究结果表明:由于菊花的抗氧化作用导致了尿液中的肌酸酐的下降,而马尿酸和苯乙酰基谷酰胺含量的上升则表明了由于菊花的抗菌作用对人体肠道菌群产生了一定的影响,而这种影响最终造成了什么效果等问题还有待进一步回答。
4.3 功能基因组的研究
代学组学应用于功能基因组学是基于这样一种观点:基因产生变异的生物体在生长速率等表型上可能没有显著的改变,这是因为细胞内的代谢物浓度的改变补偿了变异产生的影响。但是这也同时意味着生物体在代谢表型上可能会有显著的变化[108]。譬如,无论从遗传还是代谢的角度看,传统认为,Han Wistar (HW)和Sprague Dawley (SD) 两个大鼠系十分接近,而且两个系均广泛地被用于药物的研制。可是代谢组学研究发现,它们的尿液代谢组有本质的区别。Bundy等[11,109]用代谢组学方法研究蚯蚓的表型时发现,几种形态上并无区别的蚯蚓,其体腔液(coelomic fluids)和组织代谢组有明显的区别。这些例子都表现出代谢组学方法的高灵敏性。
剔除或过表达蛋白编码基因很可能导致多种代谢物的浓度发生变化,因此理论上定量研究变异产生的代谢物浓度的相对变化有可能可以识别基因产物的作用位点。另外,由于具有相似变化的基因具有相似的功能,所以可以将剔除一个未知功能的基因所产生的细胞代谢上的变化,与剔除已知功能基因所产生的代谢变化进行比较,从而确定未知基因的功能,这就为我们研究基因的生物学功能提供了理论依据和新的途径。了解基因变异带来的功能上的改变对于建立和验证新的人类疾病模型有着非常重要的意义。而且用代谢组学的方法评价基因修饰在植物改良中的安全性也有着巨大的潜力。
Raamsdonk等[19]利用FANCY(Functional ANalysis by Co-responses in Yeast)方法对野生型 FY23及其6种突变株进行了研究。这6种突变株分别是选择性剔除了 PFK26、PFK27、PET27、PET191、COX5a和ρ。在培养的指数生长中期分别对其代谢物进行提取,并获取1H NMR谱。实验数据的 PCA方法分析结果表明,代谢组学方法能对具有相关生物活性的基因进行分类,能正确地区分性质上相似、程度上不同的表型突变。甚至基因表型缄默的几种突变体也能够被明显区分为呼吸缺陷突变体、部分呼吸缺陷突变体和控制组三类。
代谢组学还参与到了 BAIR(Biological Atlas of Insulin Resistance) 计划当中。BAIR计划是由英国伦敦大学帝国理工学院、女王玛丽与威斯特菲尔德学院,剑桥大学和牛津大学合作,由英国 Wellcome Trust功能基因组发展倡议基金资助的一个项目(http://www.bair.org.uk/) ,其目标是用包括代谢组学在内的各种组学、生物信息学、啮齿动物基因打靶、人类遗传学以及结构生物学等手段,研究胰岛素作用和导致胰岛素抵抗的分子机制,并对处于正常或紊乱状态的胰岛素行为作出系统的分子描述,以对人类的迟发糖尿病、肥胖症、高血压和冠心病等疾病作出相应的解释,从而使人类能更合理、有效的处理和防止这类疾病的发生。
5 机遇和挑战
整体来讲,代谢组学研究仍然处于早期发展阶段,面临着方法学和广泛应用两方面的挑战。仪器和分析技术的发展,特别是基于计算机的模式识别和专家系统的发展将对基于 NMR的代谢研究的进步产生巨大的推进作用。但是,仍有大量方法学上的问题需要解决:生物体系的复杂性决定了生物体液以及生物组织组成的复杂性,从而造成了 NMR谱峰的重叠,对物质的归属和精确定量造成一定的影响;NMR方法的低灵敏度也是一直困扰 NMR工作者的一个问题;现有的代谢组学数据分析方法对高含量物质浓度的变化有很好的识别能力,但是对低含量代谢物分析的准确性和可靠性都较低,然而在某些情况下这些低含量的物质往往携带了重要的信息。虽然科研工作者已经得到了大量与重要生理病理变化或基因变异等有关的标志性代谢物,但是离建立完整的诊断专家系统,实现诊断常规化还有很长的距离。
尽管代谢组学的应用领域已经涉及到功能基因组学、营养学、病理学、药理学、毒理学、植物学、微生物学、昆虫/动物、系统生物学等诸多领域,但是在这些领域里的代谢组学还有许多具体应用的潜在价值可以发掘。相信随着代谢组学应用的广度和深度的不断增加,我们将会更充分认识到其优越性,这也将为人类更高效、准确的评价药物的安全性、更全面的认知疾病过程,甚至于指导人类的营养健康、监测环境等提供一种有力的手段。
参考文献
[1] H Tweeddale, L Notley-McRobb, T Ferenci. J. Bacteriol., 1998, 180: 5109~5116.
[2] J K Nicholson, J C Lindon, E Holmes. Xenobiotica, 1999, 29: 1181~1189.
[3] M E Bollard, E G Stanley, J C Lindon et al. NMR Biomed., 2005, 18: 143~162.
[4] E G Stanley, N J C Bailey, M E Bollard et al. Anal. Biochem., 2005, 343: 195~202.
[5] T M D Ebbels, E Holmes, J C Lindon et al. J. Pharm. Biomed. Anal., 2004, 36: 823~833.
[6] A W Nicholls, J K Nicholson, J N Haselden et al. Biomarkers, 2000, 5: 410~423.
[7] M Coen, E M Lenz, J K Nicholson et al. Chem. Res. Toxicol., 2003, 16: 295~303.
[8] M Coen, S U Ruepp, J C Lindon et al. J. Pharm. Biomed. Anal., 2004, 35: 93~105.
[9] N J Waters, E Holmes, C J Waterfield et al. Biochem. Pharmacol., 2002, 64: 67~77.
[10] J L Griffin, L A Walker, S Garrod et al. Comp. Biochem. Physiol. B Biochem. Mol. Biol., 2000, 127: 357~367.
[11] J G Bundy, D J Spurgeon, C Svendsen et al. FEBS Lett., 2002, 521: 115~120.
[12] J T Brindle, J K Nicholson, P M Schofield et al. Analyst, 2003, 128: 32~36.
[13] J L Griffin, S A Bonney, C Mann et al. Physiol. Genomics, 2004, 17: 140~149.
[14] J T Brindle, H Antti, E Holmes et al. Nat. Med., 2002, 8: 1439~1444.
[15] C L Gavaghan, E Holmes, E Lenz et al. FEBS Lett., 2000, 484: 169~174.
[16] C L Gavaghan, I D Wilson, J K Nicholson. FEBS Lett., 2002, 530: 191~196.
[17] R J Bino, R D Hall, O Fiehn et al. Trends Plant Sci., 2004, 9: 418~425.
[18] Fiehn, J Kopka, P Dormann et al. Nat. Biotechnol., 2000, 18: 1157~1161.
[19] L M Raamsdonk, B Teusink, D Broadhurst et al. Nat. Biotechnol., 2001, 19: 45~50.
[20] M Varnau, A Singhania. Genet. Eng. News, 2002, 22: 15.
[21] J K Nicholson, J Connelly, J C Lindon et al. Nat. Rev. Drug Discov., 2002, 1: 153~161.
[22] Fiehn. Plant Mol.Biol., 2002, 48: 155~171.
[23] J L Griffin, J P Shockcor. Nat. Rev. Cancer, 2004, 4: 551~561.
[24] A R Fernie, R N Trethewey, A J Krotzky et al. Nat. Rev. Mol. Cell Biol., 2004, 5: 763~769.
[25] J T Brindle, H Antti, E Holmes et al. Nat. Med., 2002, 8: 1439~1444.
[26] J Allen, H M Davey, D Broadhurst et al. Nat. Biotechnol., 2003, 21: 692~696.
[27] H Jenkins, N Hardy, M Beckmann et al. Nat. Biotechnol., 2004, 22: 1601~1606.
[28] J K Nicholson, E Holmes, J C Lindon et al. Nat. Biotechnol., 2004, 22: 1268~1274.
[29] A Macchiarulo, I Nobeli, J M Thornton. Nat. Biotechnol., 2004, 22: 1039~1045.
[30] M Brazil. Nat. Rev. Drug Discov., 2003, 2: 169~169.
[31] J K Nicholson, I D Wilson. Nat. Rev. Drug Discov., 2003, 2: 668~676.
[32] R B Stoughton, S H Friend. Nat. Rev. Drug Discov., 2005, 4: 345~350.
[33] W Weckwerth. Annu. Rev. Plant Biol., 2003, 54: 669~689.
[34] D A Fell. Trends Genet., 2001, 17: 680~682.
[35] L L Smith. Trends Pharmacol. Sci., 2001, 22: 281~285.
[36] S Ekins, Y Nikolsky, T Nikolskaya. Trends Pharmacol. Sci., 2005, 26: 202~209.
[37] N T Wood. Trends Plant Sci., 2001, 6: 191~191.
[38] J Memelink. Trends Plant Sci., 2005, 10: 305~307.
[39] S K Herbert. Proc. Natl. Acad. Sci. U. S. A., 2002, 99: 12518~12519.
[40] J D Mougous, M D Leavell, R H Senaratne et al. Proc. Natl. Acad. Sci. U. S. A., 2002, 99: 17037~17042.
[41] A Zewail, M W Xie, Y Xing et al. Proc. Natl. Acad. Sci. U. S. A., 2003, 100: 3345~3350.
[42] J Browse, B M Lange. Proc. Natl. Acad. Sci. U. S. A., 2004, 101: 14996~14997.
[43] D R Janero, N S Bryan, F Saijo et al. Proc. Natl. Acad. Sci. U. S. A., 2004, 101: 16958~16963.
[44] Y L Wang, E Holmes, J K Nicholson et al. Proc. Natl. Acad. Sci. U. S. A., 2004, 101: 12676~12681.
[45] D Cook, S Fowler, O Fiehn et al. Proc. Natl. Acad. Sci. U. S. A., 2004, 101: 15243~15248.
[46] W Weckwerth, M E Loureiro, K Wenzel et al. Proc. Natl. Acad. Sci. U. S. A., 2004, 101: 7809~7814.
[47] M Y Hirai, M Yano, D B Goodenowe et al. Proc. Natl. Acad. Sci. U. S. A., 2004, 101: 10205~10210.
[48] J E Ippolito, J Xu, S J Jain et al. Proc. Natl. Acad. Sci. U. S. A., 2005, 102: 9901~9906.
[49] G S Catchpole, M Beckmann, D P Enot et al. Proc. Natl. Acad. Sci. U. S. A., 2005, 102: 14458~14462.
[50] C Kristensen, M Morant, C E Olsen et al. Proc. Natl. Acad. Sci. U. S. A., 2005, 102: 1779~1784.
[51] H Bono, I Nikaido, T Kasukawa et al. Genome Res., 2003, 13: 1345~1349.
[52] O C Yoder, B G Turgeon. Curr. Opin. Plant Biol., 2001, 4: 315~321.
[53] M Fehr, D W Ehrhardt, S Lalonde et al. Curr. Opin. Plant Biol., 2004, 7: 345~351.
[54] E Fridman, E Pichersky. Curr. Opin. Plant Biol., 2005, 8: 242~248.
[55] J L Griffin. Curr. Opin. Chem. Biol., 2003, 7: 648~654.
[56] J van der Greef, P Stroobant, R van der Heijden. Curr. Opin. Chem. Biol., 2004, 8: 559~565.
[57] H O Villar, J L Yan, M R Hansen. Curr. Opin. Chem. Biol., 2004, 8: 387~391.
[58] J Minshull, J E Ness, C Gustafsson et al. Curr. Opin. Chem. Biol., 2005, 9: 202~209.
[59] A Saghatelian, B F Cravatt. Curr. Opin. Chem. Biol., 2005, 9: 62~68.
[60] D Seo, G S Ginsburg. Curr. Opin. Chem. Biol., 2005, 9: 381~386.
[61] M Morris, S M Watkins. Curr. Opin. Chem. Biol., 2005, 9: 407~412.
[62] D B Kell, R D King. Trends Biotechnol., 2000, 18: 93~98.
[63] T M Kutchan. Trends Biotechnol., 2005, 23: 381~383.
[64] S G Villas-Boas, S Rasmussen,G A Lane. Trends Biotechnol., 2005, 23: 385~386.
[65] M J van der Werf. Trends Biotechnol., 2005, 23: 11~16.
[66] C Birkemeyer, A Luedemann, C Wagner, et al. Trends Biotechnol., 2005, 23: 28~33.
[67] D Edwards, J Batley. Trends Biotechnol., 2004, 22: 232~237.
[68] R Goodacre, S Vaidyanathan, W B Dunn et al. Trends Biotechnol., 2004, 22: 245~252.
[69] A M Burja, S Dhamwichukorn, P C Wright. Trends Biotechnol., 2003, 21: 504~511.
[70] P Brazhnik, A de la Fuente, P Mendes. Trends Biotechnol., 2002, 20: 467~472.
[71] G H Thomas. Trends Biotechnol., 2001, 19: 126~127.
[72] M Tomita. Trends Biotechnol., 2001, 19: 205~210.
[73] T J Phelps, A V Palumbo, A S Beliaev. Curr. Opin. Biotechnol., 2002, 13: 20~24.
[74] B van Ommen,R Stierum. Curr. Opin. Biotechnol., 2002, 13: 517~521.
[75] M Arita, M Robert, M Tomita. Curr. Opin. Biotechnol., 2005, 16: 344~349.
[76] K M Oksman-Caldentey, K Saito. Curr. Opin. Biotechnol., 2005, 16: 174~179.
[77] M Stitt, A R Fernie. Curr. Opin. Biotechnol., 2003, 14: 136~144.
[78] G Hofmann, M McIntyre, J Nielsen. Curr. Opin. Biotechnol., 2003, 14: 226~231.
[79] S M Watkins, J B German. Curr. Opin. Biotechnol., 2002, 13: 512~516.
[80] W Weckwerth, O Fiehn. Curr. Opin. Biotechnol., 2002, 13: 156~160.
[81] D Delneri, F L Brancia, S G Oliver. Curr. Opin. Biotechnol., 2001, 12: 87~91.
[82] L Aicher, D Wahl, A Arce et al. Electrophoresis, 1998, 19: 1998~2003.
[83] M J Geisow. Nat. Biotechnol., 1998, 16: 206~206.
[84] N L Anderson, J Taylor, J P Hofmann et al. Toxicol. Pathol., 1996, 24: 72~76.
[85] J K Nicholson, E Holmes, I D Wilson. Nat. Rev. Microbiol., 2005, 3: 431~438.
[86] J Xu, J I Gordon. Proc. Natl. Acad. Sci. USA, 2003, 100: 10452~10459.
[87] J C Lindon, E Holmes, J K Nicholson. Prog. Nucl. Magn. Reson. Spectrosc., 2001, 39: 1~40.
[88] Y L Wang, M E Bollard, H Keun et al. Anal. Biochem., 2003, 323: 26~32.
[89] M Rooney, J Troke, J K Nicholson et al. Magn. Reson. Med., 2003, 50: 925~930.
[90] H Vilca-Melendez, I F Duarte, R Girlanda et al. Hepatology, 2005, 42: 338A~338A.
[91] P K Valonen, J L Griffin, K K Lehtimaki et al. NMR Biomed., 2005, 18: 252~259.
[92] T M Tsang, J L Griffin, J Haselden et al. Magn. Reson. Med., 2005, 53: 1018~1024.
[93] E M Ratai, S Pilkenton, M R Lentz et al. NMR Biomed., 2005, 18: 242~251.
[94] J L Taylor, C L Wu, D Cory et al. Magn. Reson. Med., 2003, 50: 627~632.
[95] C L Wu, J L Taylor, W L He et al. Magn. Reson. Med., 2003, 50: 1307~1311.
[96] M A Burns, W L He, C L Wu et al. Technol. Cancer Res. Treat., 2004, 3: 591~598.
[97] B M Beckwith-Hall, N A Thompson, J K Nicholson et al. Analyst, 2003, 128: 814~818.
[98] H R Tang, Y L Wang, J K Nicholson et al. Anal. Biochem., 2004, 325: 260~272.
[99] L H Lucas, C K Larive, P S Wilkinson et al. J. Pharm. Biomed. Anal., 2005, 39: 156~163.
[100] J C Lindon, J K Nicholson, E Holmes et al. Toxicol. Appl. Pharmacol., 2003, 187: 137~146.
[101] J C Lindon, H C Keun, T M D Ebbels et al. Pharmacogenomics, 2005, 6: 691~699.
[102] M A Constantinou, E Papakonstantinou, M Spraul et al. Anal. Chim. Acta, 2005, 542: 169~177.
[103] M A Constantinou, E Papakonstantinou, D Benaki et al. Anal. Chim. Acta, 2004, 511: 303~312.
[104] S H Moolenaar, U F H Engelke, R A Wevers. Ann. Clin. Biochem., 2003, 40: 16~24.
[105] K Odunsi, R Wollman, C Ambrosone et al. J. Soc. Gynecol. Invest., 2004, 11: 70A~70A.
[106] K S Solanky, N J Bailey, B M Beckwith-Hall et al. J. Nutr. Biochem., 2005, 16: 236~244.
[107] Y L Wang, H R Tang, J K Nicholson et al. J. Agric. Food Chem., 2005, 53: 191~196.
[108] B Teusink, F Baganz, H V Westerhoff et al. Method Microbiol., 1998, 26: 297~336.
[109] J G Bundy, E M Lenz, N J Bailey et al. Environ. Toxicol. Chem., 2002, 21: 1966~1972.
注:本文为提供者整理翻译的,由于知识所限,错误在所难免,敬请原谅。如有问题可以查找原文。



 沪公网安备 31010602001115号
沪公网安备 31010602001115号